A Graph a Day
Vor einiger Zeit habe ich @randomGraphs geschrieben: Ein Twitterbot, der einen Zufallsgraphen pro Tag tweetet.
Die meisten Graphtypen, die er darstellen kann stammen aus der NetworkX Bibliothek oder sind reale Netzwerke. Ein paar Proximity Graphs habe ich selbst geschrieben. Die Darstellung und gegebenenfalls das Layout übernimmt Cytoscape oder graph-tool (dessen Autor diesem Bot folgt).
Bei diesem Projekt habe ich exzessiv Gebrauch von Pythons Decorator und
Introspection gemacht, sodass man, um einen neuen Graphtyp einzuführen
nur eine Methode schreiben muss, die eine Graph-Datenstruktur zurück gibt.
Einstellungen, welche Darstellungen erlaubt sind, werden per decorator
getätigt und alle Methoden werden per Introspection automatisch zum Pool
hinzugefügt, aus dem der Zufallsgenerator zieht.
Eine typische Methode sieht etwa so aus.
@synonym("Barabasi Albert")
@synonym("preferential attachment")
@style(styles_all)
@layout(["kamada-kawai", "force-directed", "sfdp", "fruchterman_reingold", "arf", "radial_tree"])
def generateBarabasiAlbert(self, N=None, m=None, **kwargs):
if N is None: N = random.randint(4, 400)
if m is None: m = random.randint(1, 5)
G = gen.barabasi_albert_graph(N, m) # gen is networkx Generator
details = dict(name="Barabási-Albert Graph", N=N, m=m, seed=self.seed,
template="{name}, N = {N}, m = {m}")
return G, details
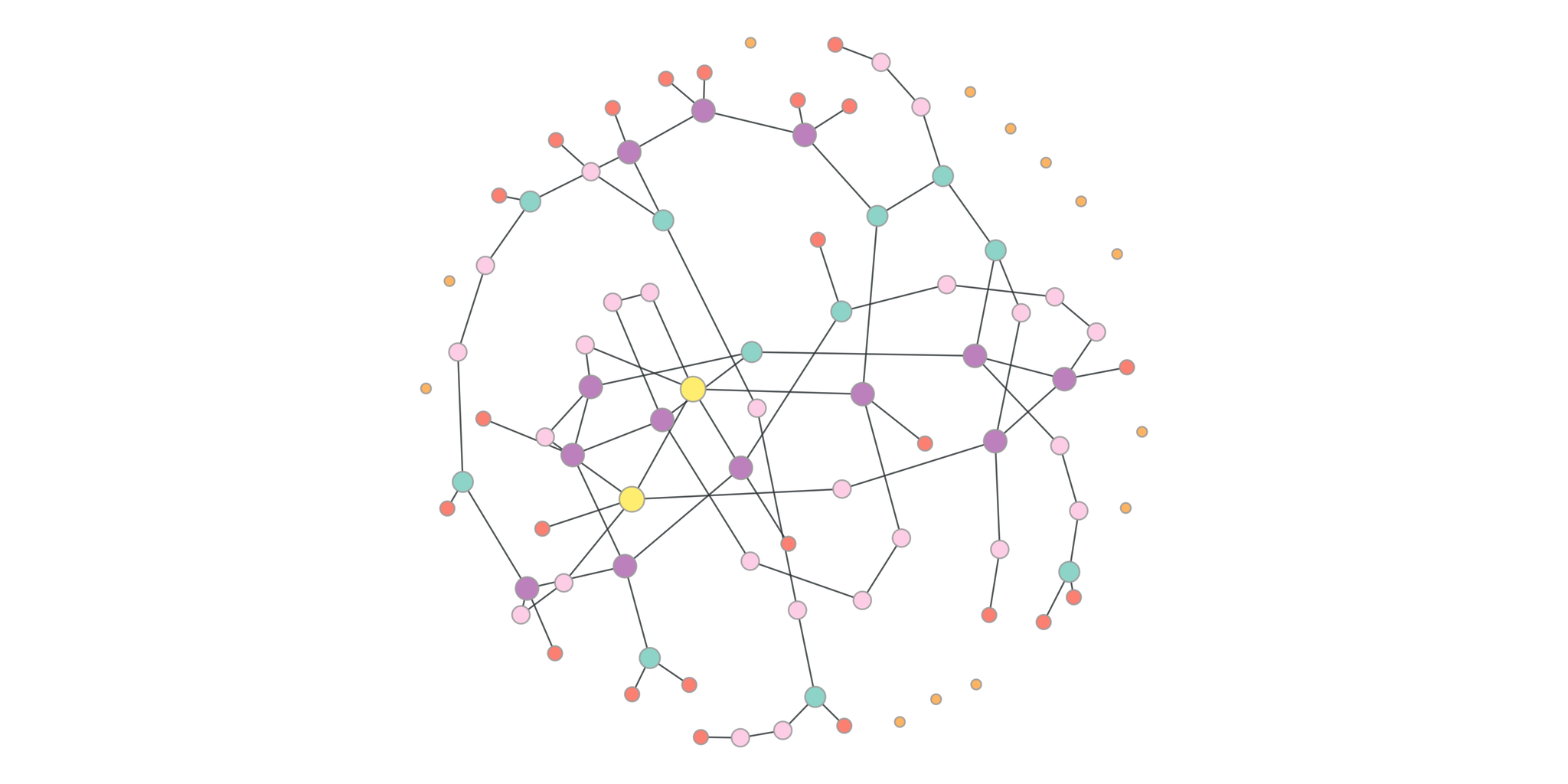
Und liefert für $N=226, m=1$ und das radial_tree Layout beispielsweise
diesen Graph. Die Größe der Knoten wird hier von der
Betweenness Centrality bestimmt.

Die @synonym Decorators ermöglichen die zweite Funktion des Bots, denn
er tweetet nicht nur einmal am Tag einen zufälligen Graphen, sondern reagiert
auch auf Mentions. Falls in der Mention der Name der Methode oder eines der
per @synonym registrierten Worte auftaucht, antwortet er mit einem Bild des
entsprechenden Graphen. Dank fuzzywuzzy ist es sogar resistent gegen Tippfehler.
Twitter unterstützt leider keine Vektorgrafiken und wandelt Bilder gerne in
stark komprimierte .jpg, was gerade bei diesen Graphen zu störenden
Artefakten führt. Dagegen hilft es, wenn ich einen Rand aus transparenten
Pixeln dem Bild hinzufüge. Das führt dazu, dass Twitter .jpg nicht als
geeignetes Format ansieht und die Bilder im verlustfreien .png ausliefert.
convert -alpha on -channel RGBA -bordercolor "rgba(0,0,0,0)" -border "1x1" input.png output.png
Der komplette Quellcode ist auf Github.